
Недостаточное число прочтений или отсутствие прочтений с одной цепей не позволяет нам отличить истинный вариант от ошибки секвенирования.
Опасность SB в получении ложноположительных или ложноотрицательных результатов.
SB возникает как при таргетном, так и при полногеномном секвенировании.
Пример SB в сиквенсе
Наглядный пример – регион chr21:7,774,473-7,776,655 генома NIST8398 из проекта Genome in a Bottle (https://jimb.stanford.edu/giab-resources).
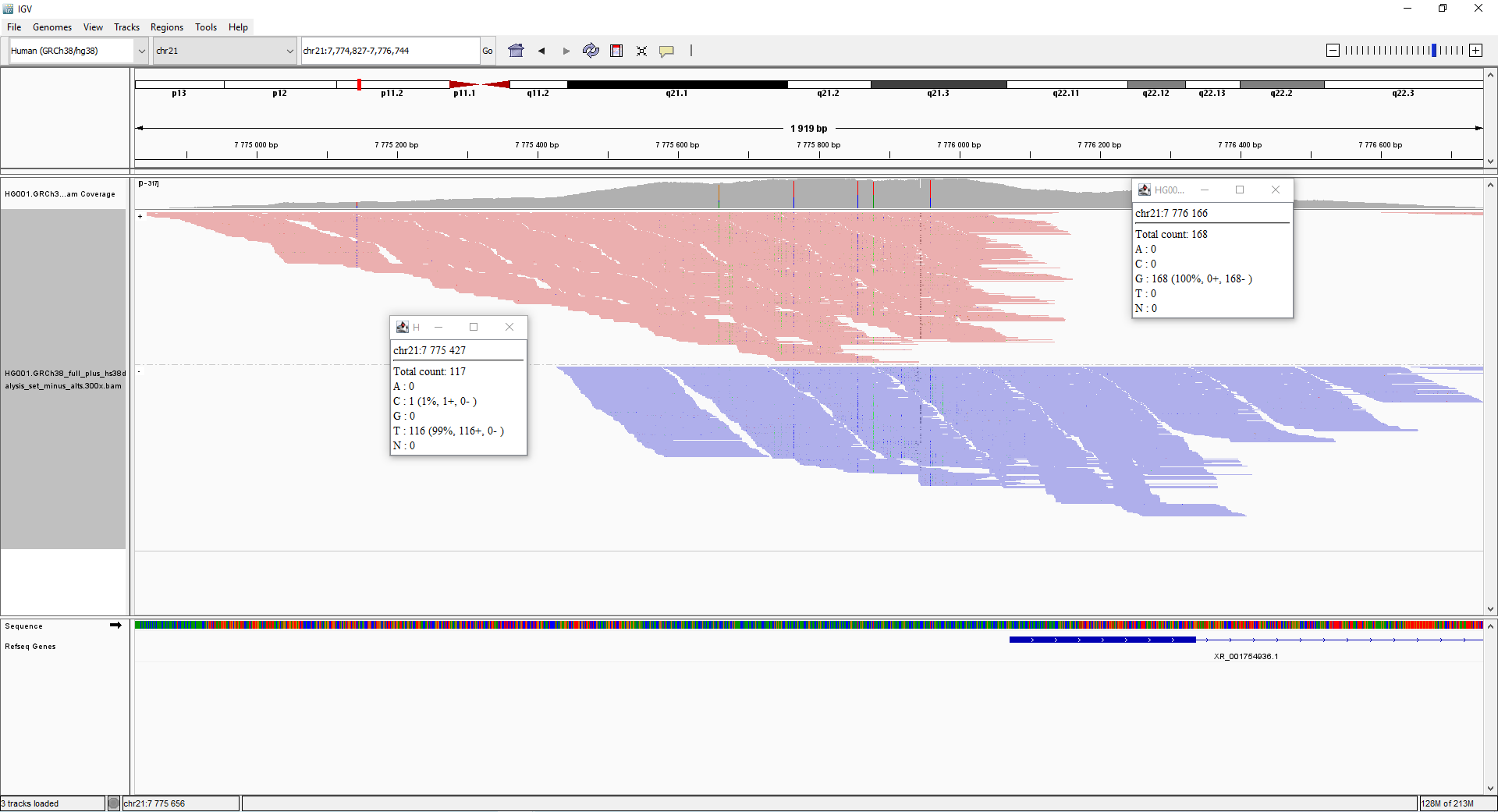
Регионы со Strand Bias в сиквенсе референсного образца NIST8398.
Вероятно, при подготовке полногеномной библиотеки этот участок был недостаточно расщеплен. Были получены фрагменты длинной до 1111 п.н., что при парноконцевом прочтении 150 + 150 привело к SB.
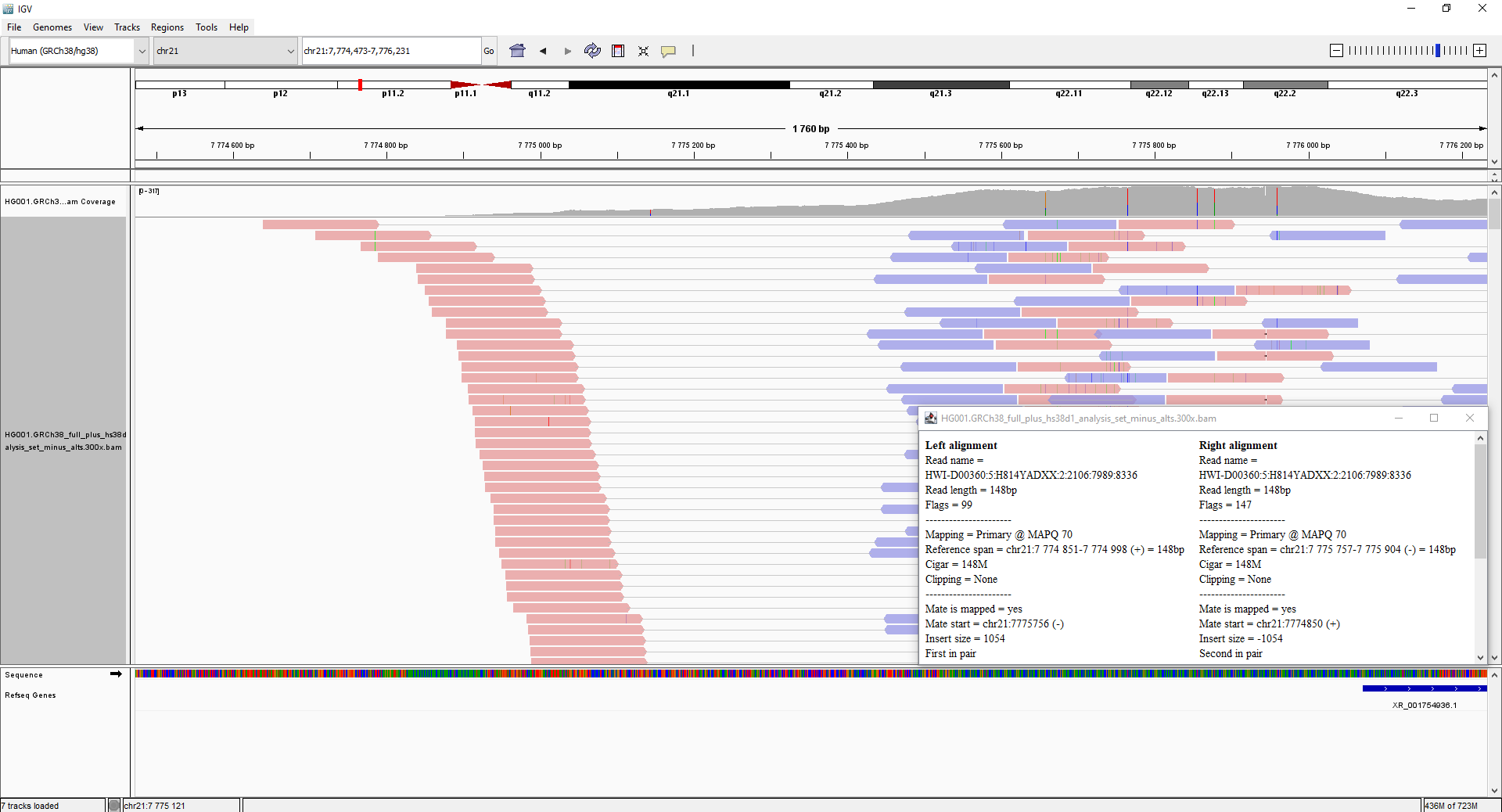
Парноконцевые прочтения длиной 150 п.н. не перекрывают фрагменты ДНК более 1000 п.н. Возникает протяженный регион SB.
Более подробно о том почему возникает и какие ошибки скрывает SB в следующих публикациях.
